液滴型单细胞测序技术比较(二)
共 1228字,需浏览 3分钟
·
2021-05-29 04:57

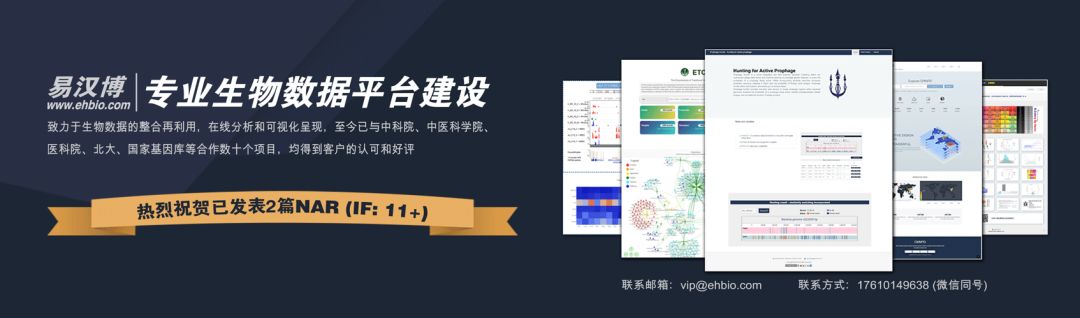
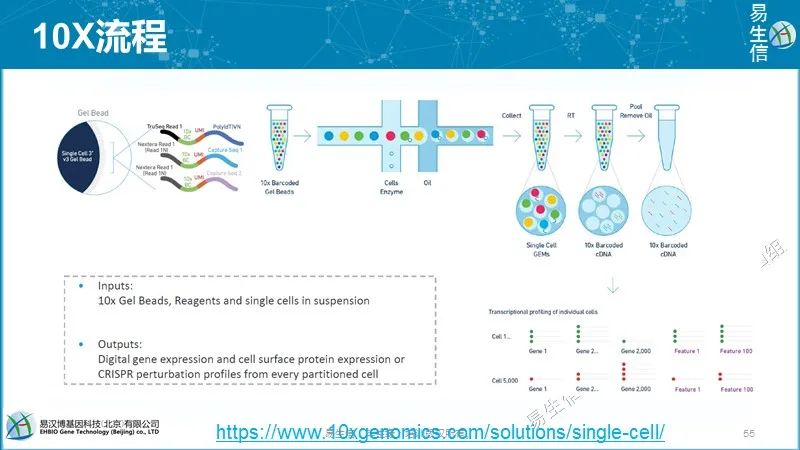
三种液滴型方法采用相似的技术生成液滴,采用barcode标记细胞,应用UMI进行偏好校正。但它们在beads的 、barcode的设计、cDNA扩增等不同。
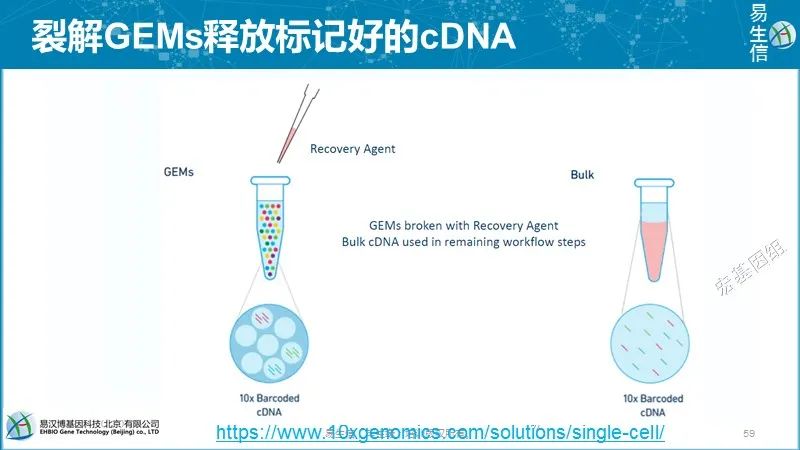
10X和inDrop采用水凝胶beads,因此引物可以固定在beads里面,而Drop-seq的引物只能固定在beads表面。包裹到液滴后,10X的beads发生溶解,引物释放到溶液中可以提高mRNA的捕获效率。inDrop使用紫外诱导的切割技术释放引物。而DropSeq的引物不能从beads释放,会降低其mRNA捕获效率。
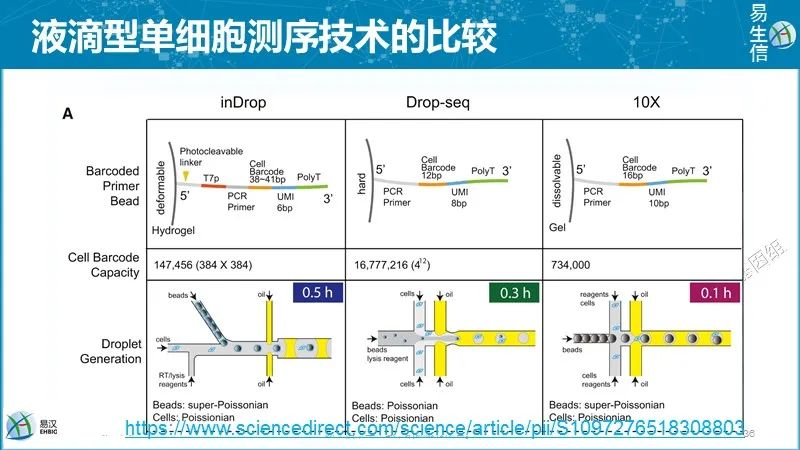
inDrop和10X的反转录等过程都在液滴内进行,有利于提高效率和降低试剂消耗。inDrop采用体外转录方式进行扩增,需要时间比较久。
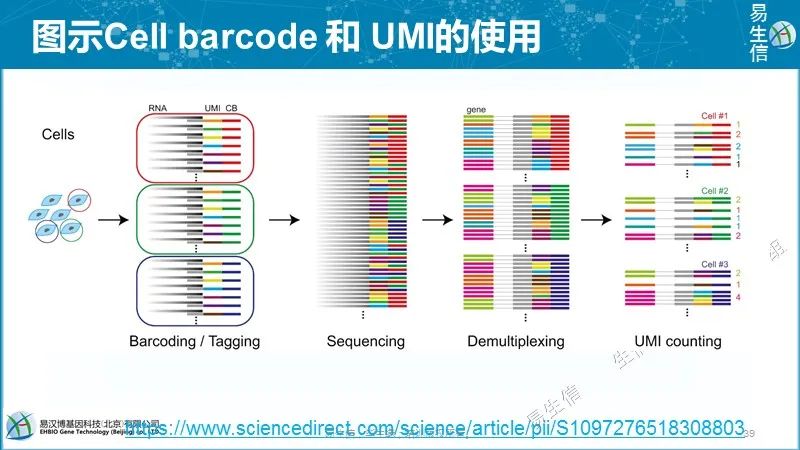
单细胞里面两个最重要的序列标示。
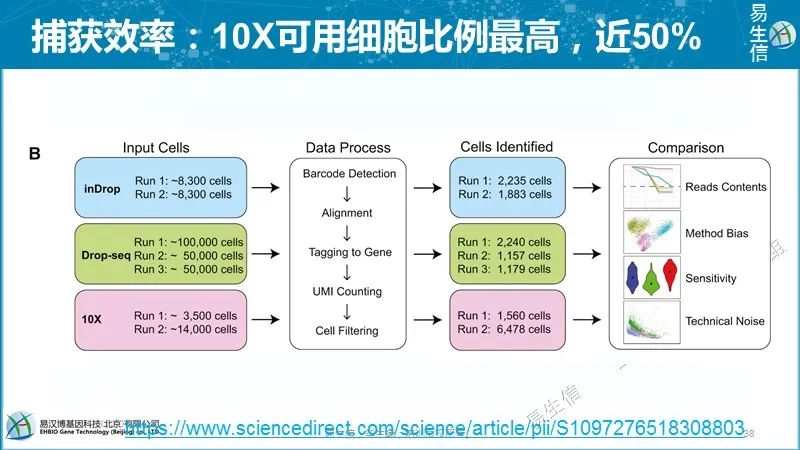
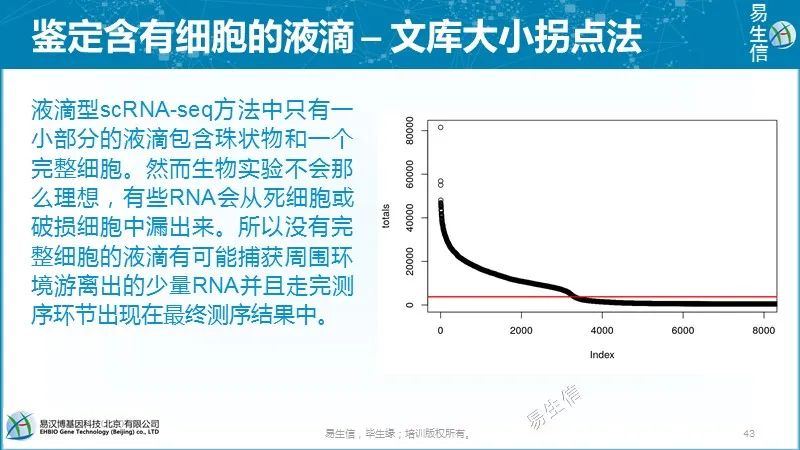
液滴型scRNA-seq方法中只有一小部分的液滴包含珠状物和一个完整细胞。然而生物实验不会那么理想,有些RNA会从死细胞或破损细胞中漏出来。所以没有完整细胞的液滴有可能捕获周围环境游离出的少了RNA并且走完测序环节出现在最终测序结果中。液滴大小、扩增效率和测序环节中的波动会导致“背景”和真实细胞最终获得的文库大小变化很大,使得区分哪些文库来源于背景哪些来源于真实细胞变得复杂。
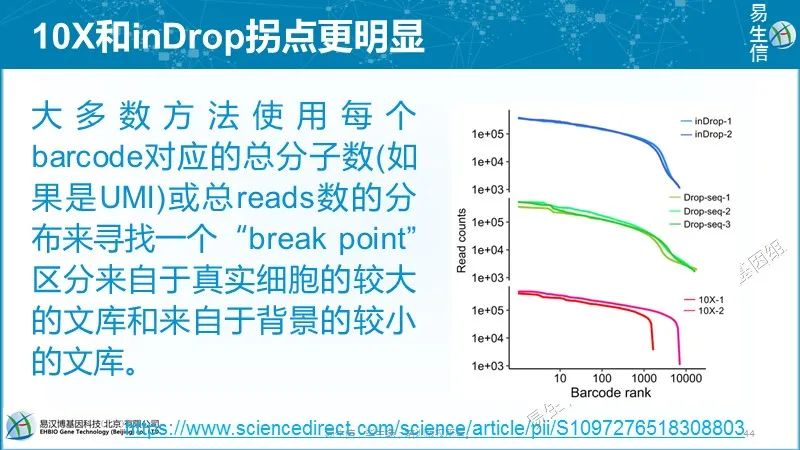
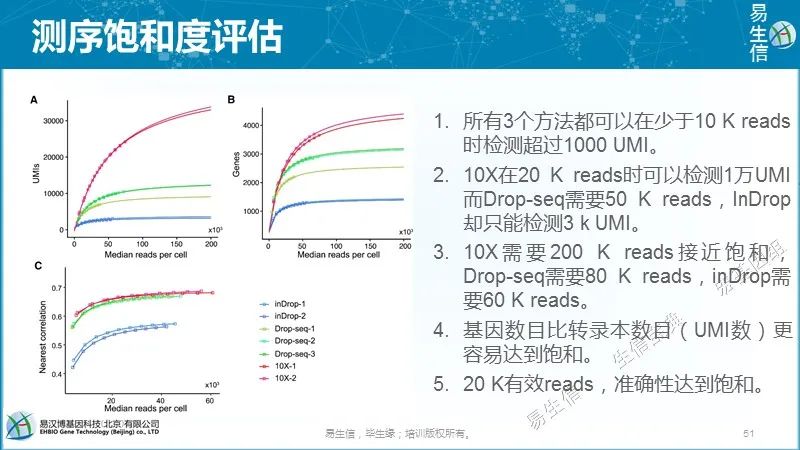
大多数方法使用每个barcode对应的总分子数(如果是UMI)或总reads数的分布来寻找一个“break point”区分来自于真实细胞的较大的文库和来自于背景的较小的文库。
CellRanger假设真实细胞文库大小变化在10倍以内,用期望的细胞数目估计区间的分布。

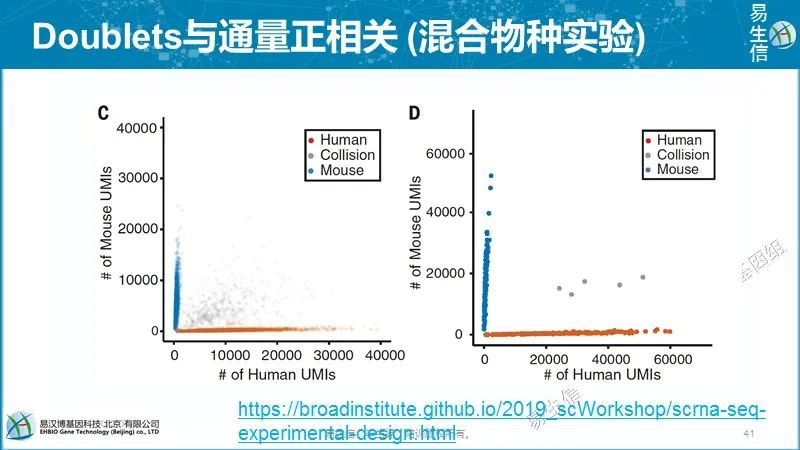
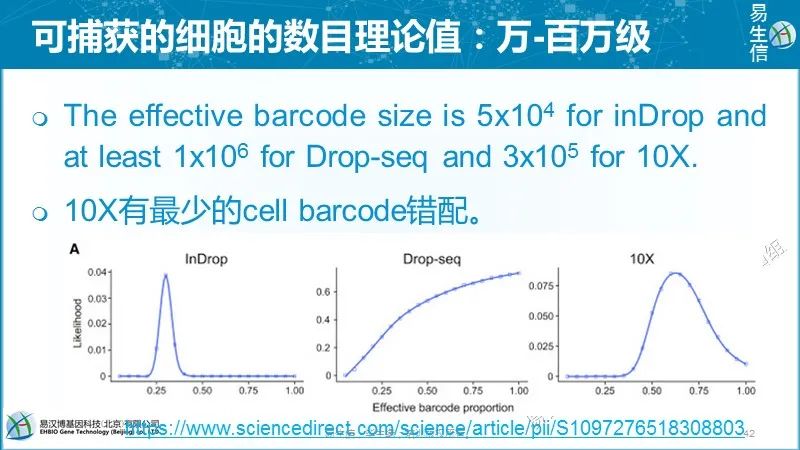
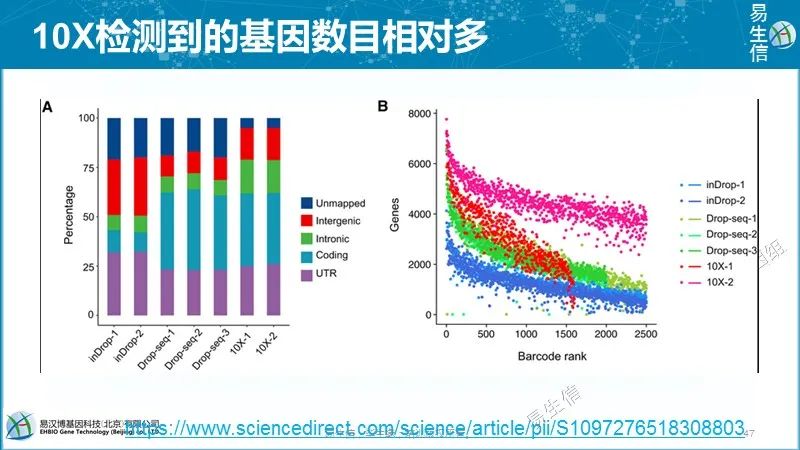
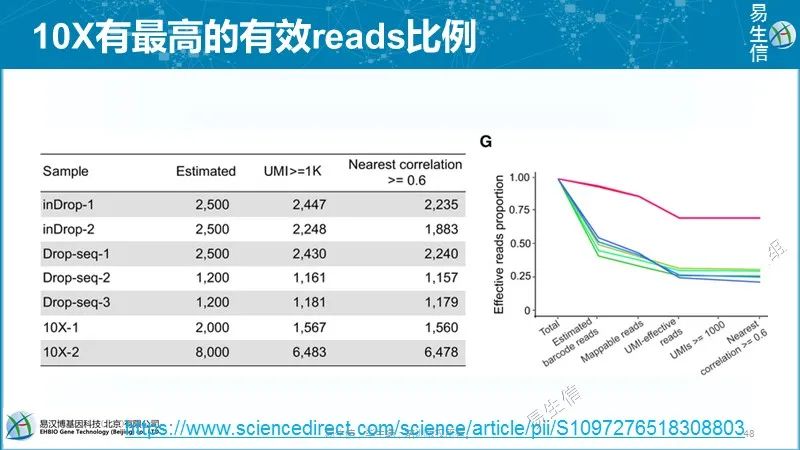
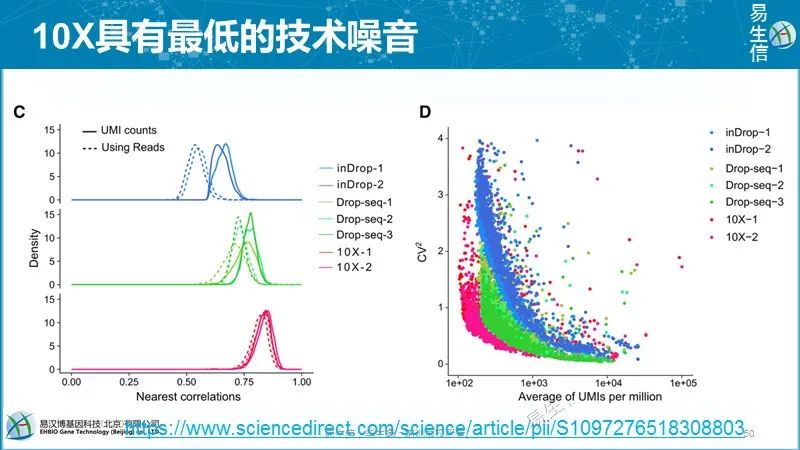
因为采用的是近乎同质性的细胞和持家基因,认为具有最小噪音的基因集的变化分布与其它基因类似,因此可以认为细胞总的变化反应了技术噪音的水平。技术噪音采用spearman correlation分析,相似值越小说明技术噪音越大。而且分别用UMI和readscount做了评估,10X数据两个评估结果类似,InDrop技术UMI的技术噪音小一些。
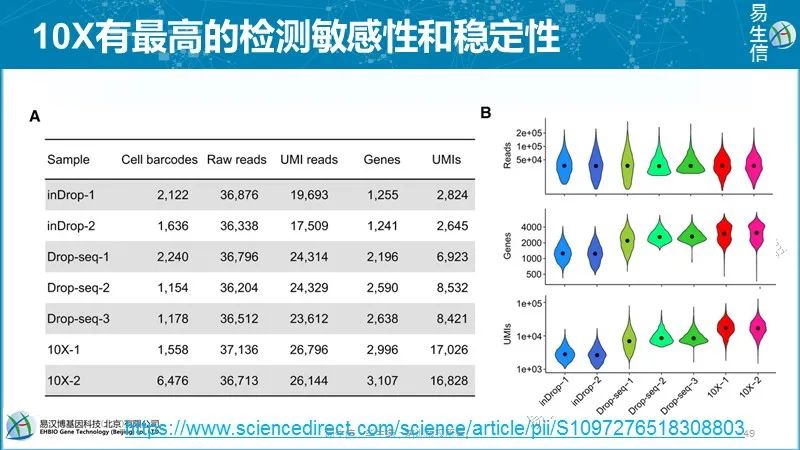
基因水平的技术变化可以通过标准化的UMI的变异系数(coefficient of variation, CV)进行评估。总体来看,高表达基因对额CV值小,有更小的技术噪音。10X技术技术噪音依然最小。值得注意的是,一些最高表达的基因噪音水平却比较高,右上的这些点。查看了下,主要是各个细胞里面最高表达的基因或线粒体基因,高的噪音可能来源于转录随机性。




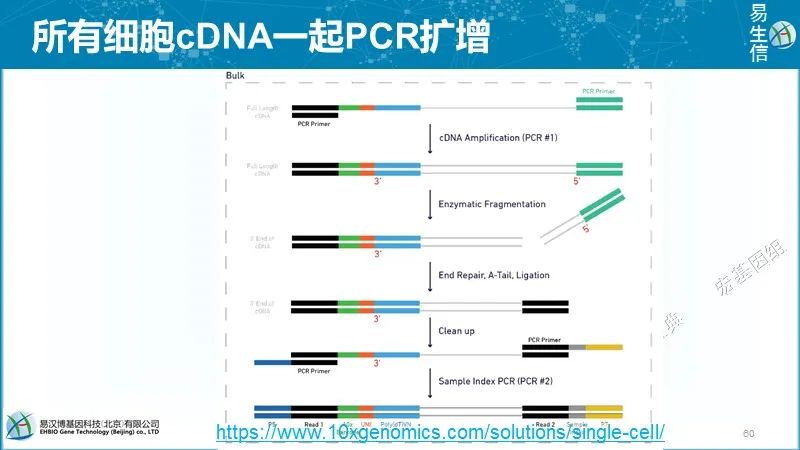

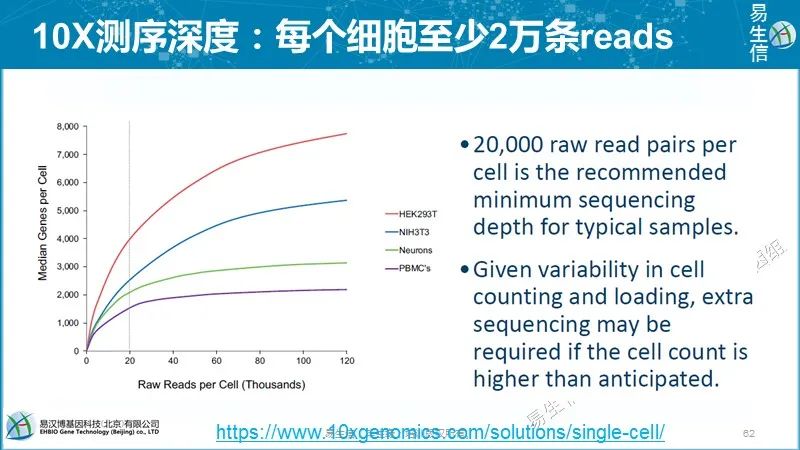
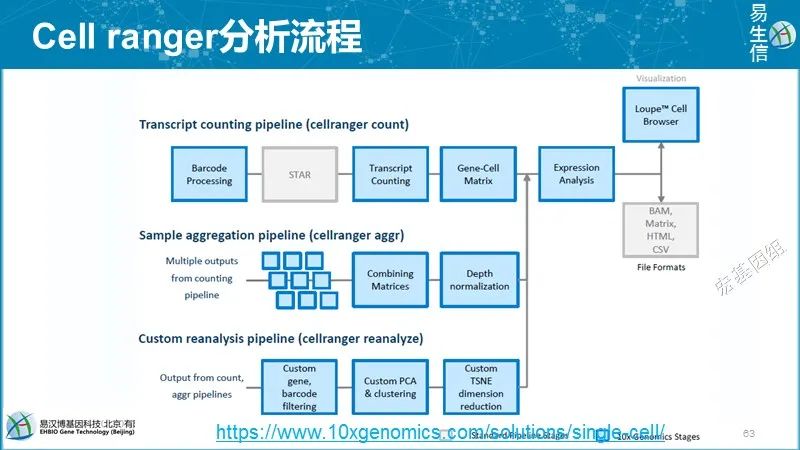
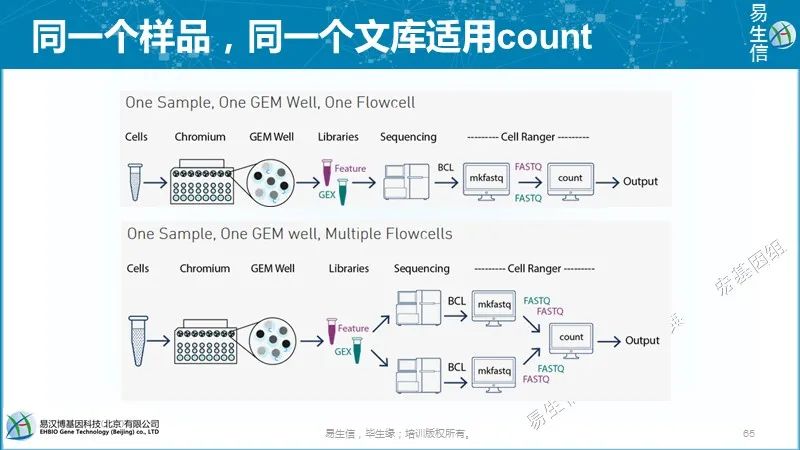
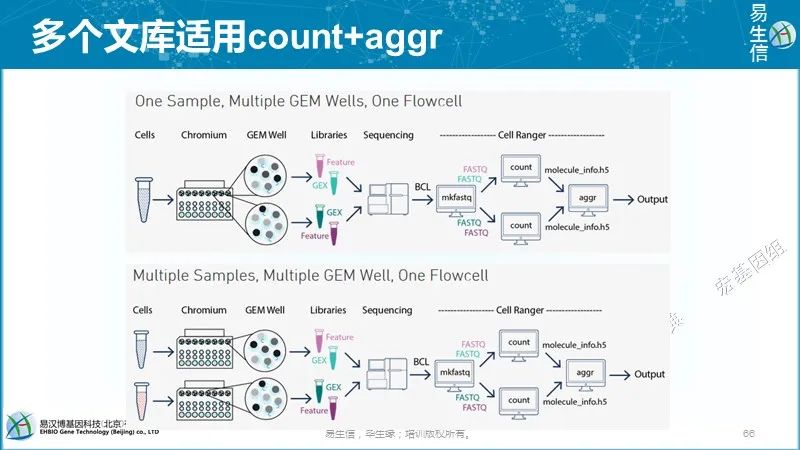
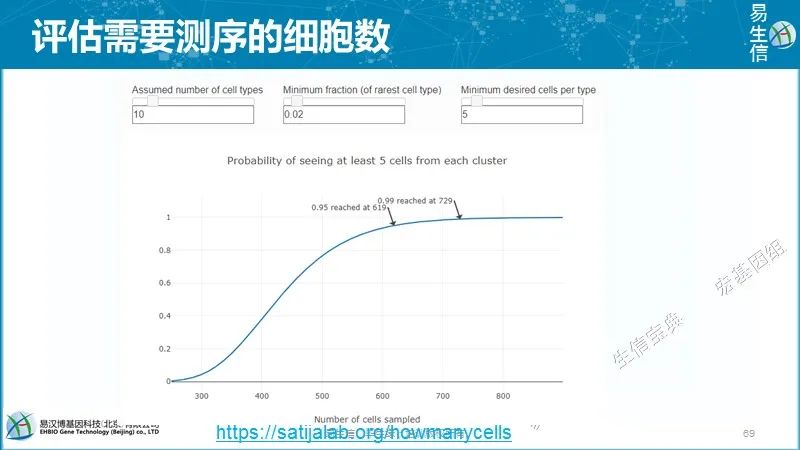
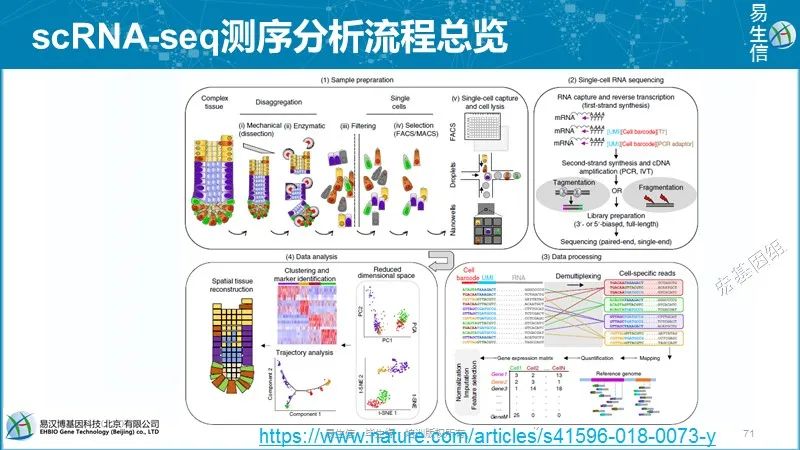
10X单细胞测序分析软件:Cell ranger,从拆库到定量




往期精品(点击图片直达文字对应教程)
后台回复“生信宝典福利第一波”或点击阅读原文获取教程合集